il sequenziamento del dna è una tecnica indispensabile in biologia e medicina perché permette di conoscere l'esatta sequenza di nucleotidi di una molecola di dna negli anni settanta del novecento fredericks hunger mise a punto metodo chi ha premesso di sequenziare frammenti di dna o interi genomi immaginiamo di dover sequenziare solo una porzione di dna prima è necessario amplificarlo cioè averne molte copie per farlo si ricorre alla pcr reazione a catena della polimerasi a questo punto le copie amplificate devono essere denaturate i due filamenti vengono separati grazie a un aumento della temperatura si aggiungono poi altri ingredienti
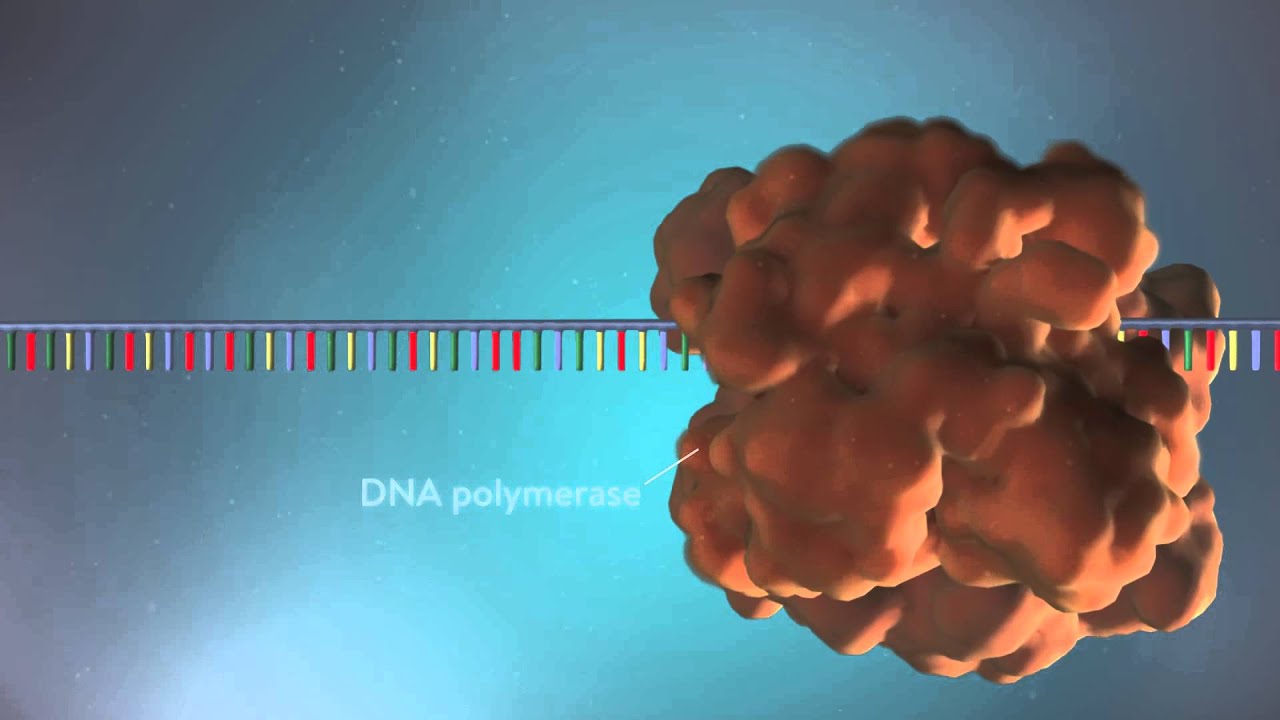
alla miscela uno è la dna polimerasi benzema che sintetizza un nuovo filamento di dna a partire dal filamento stampo per avviare la sintesi è necessario anche un primer un oligo nucleotide prodotto ad hoc per legarsi al dna da sequenziare e servono le unità che compongono il dna cioè i tesori ribot nucleo tv trifosfato che trasportano le quattro basi azotate adenina timina guanina citosina se aggiunge infine una piccola quantità di nucleotidi modificati la modifica riguarda lo zucchero che compone il nucleotide rispetto ai desossiribonucleico vi manca il gruppo seadrill è in posizione 3 primo come vedremo tra
poco la chiave del metodo di sequenziamento e proprio in questa piccola differenza il nucleotide modificato anche un'altra particolarità è legato a un marcatore fluorescente indispensabile per poter vedere il risultato si usano marcatori fluorescenti di quattro colori diversi uno per ciascun tipo di base a giocata completata la miscela si avvia la sintesi di un nuovo filamento di dna la dna polimerasi si lega al primer e aggiunge un nucleotide alla volta sempre rispettando la regola della complementarietà delle il nuovo filamento si allunga finché sono aggiunti nucleotidi normali ma quando ne inserito uno modificato la sintesi si arresta
la mancanza del gruppo sideri le impedisce infatti la formazione di un legame con il nucleotide successivo e provoca il distacco della dna polimerasi il risultato di questa fase è la formazione di un frammento di dna a doppio filamento che all'ultimo nucleotide marcato l'interruzione della sintesi elemento cruciale del metodo di senger e che perciò è chiamato metodo terminazione di catena l'inserimento di un nucleotide modificato è dovuto al caso per cui anche la lunghezza del filamento sintetizzato risulta casuale ma se la sintesi avviene tante volte grazie alle copie prodotte con la pcr avremo filamenti di tutte le
lunghezze possibili di poche basi o lunghi quanto l'intera porzione di dna da sequenziare nella fase successiva si di natura nuovamente il dna i singoli filamenti vengono quindi sottoposti ad elettroforesi capillare con questa tecnica la miscela è inserita in un capillare a cui applicato un campo elettrico i frammenti di dna grazie alle loro cariche negative cominciano a migrare verso il polo positivo i più corti migrano più velocemente quindi possiamo confrontare la lunghezza dei frammenti in base alla loro velocità al termine della corsa elettroforetiche un laser e cita i marcatori fluorescenti legate ai nucleotidi modificati e un
rivelatore registra il tipo di luce emessa abbiamo così tutti gli elementi per ricostruire la sequenza a ciascuno dei quattro colori corrisponde una diversa base azotata la sequenza così ottenuta è complementare alla sequenza che si voleva conoscere lo stesso procedimento può essere usato per ottenere la sequenza di un intero genoma per far ciò il genoma e prima frammentato e il sequenziamento eseguito sui singoli frammenti i risultati sono elaborati da un software che trova i punti di sovrapposizione e ricostruisce la sequenza completa anche in questo caso la sequenza che si ottiene è complementare alla sequenza ricercata in
questo modo gli scienziati sono riusciti a sequenziare il genoma umano oltre a quello di molti altri organismi nel corso degli anni sono stati messi a punto nuovi metodi di sequenziamento più veloci ed economici molti dei quali però si basano ancora sul metodo inventato da sanger